Deel dit project
Expanding the Epi-Discovery Tool Box
Samenvatting
Het eukaryotische genoom zit verpakt in chromatine: een structuur bestaande uit DNA, histonen en bijbehorende eiwitten. Er bestaan 4 kernhistonen, H2A, H2B, H3 en H4, en een linkerhiston, H1. De vier kernhistonen vormen samen een octamere histonkern, waar het DNA omheen gewikkeld zit. Samen vormen het DNA en de histonkern een nucleosoom; de structurele basiseenheid van chromatine. Histon H1 bindt vervolgens aan zogeheten ‘linkergebieden’ tussen de nucleosomen. Door deze binding wordt elk nucleosoom aan zijn buren verbonden waardoor een geordende fiber onstaat: de chromatinefiber. De basisstructuur van de chromatinefiber is min of meer gelijk in het hele genoom. Wel kunnen de dichtheid van nucleosomen, hun post-translationele modificaties, en de eiwitten die aan chromatine gebonden zijn varieren, waardoor verschillende chromatinetoestanden kunnen ontstaan. Hoofdstuk 1 beschrijft deze variatie en de daarmee gepaard gaande uitdagingen bij het begrijpen van algemene principes rondom chromatine, zoals de rol van chromatine en genexpressie, het behoud van de structuur van chromatine tijdens DNA transcriptie en DNA reparatie, en de ruimtelijke en temporale coordinatie van chromatinestructuur en DNA replicatie.
Voor een goed begrip van chromatine is het essentieel om te weten hoe de chromatinetoestanden op verschillende plekken in het genoom worden gereguleerd en welke factoren daarbij een rol spelen. Daarom richt dit proefschrift zich op het ontrafelen van locus-specifieke chromatineregulatie en chromatine-eiwitdynamiek.
In hoofdstuk 2 wordt Epi-ID beschreven. Met deze techniek, ontwikkeld voor gebruik in gist, kan in parallel voor duizenden genetische mutanten worden bepaald wat de chromatinetoestand is. Epi-ID maakt gebruik van korte DNA sequenties – DNA barcodes. In een collectie giststammen, met elk een specifieke mutatie, wordt in elke stam op dezelfde genomische locatie een unieke barcode geintroduceerd. Vervolgens wordt op de hele collectie chromatine-immunoprecipitatie uitgevoerd. Door in het geprecipiteerde materiaal met behulp van ‘high-throughput sequencing’ te tellen hoe vaak elke barcode voorkomt, wordt bepaald hoevaak een bepaalde chromatinekenmerk in elk van de mutanten voorkomt. Epi-ID kan voor een breed scala aan chromatinemodificaties en chromatineeiwitten worden toegepast. Hoofdstuk 3 beschrijft hoe Epi-ID gebruikt kan worden om factoren te identificeren die verantwoordelijk zijn voor het reguleren van de hoeveelheid H2A.Z. Dit is een histonvariant die een of beide kopien van het H2A kernhiston vervangt in nucleosomen die zich naast promoters van genen bevinden. Met Epi-ID werd bepaald dat SWR1 de belangrijkste regulator is van de verhouding van H2A versus H2A.Z. SWR1 is een ATP-afhankelijk chromatineremodelleringscomplex waarvan bekend is dat het H2A kan vervangen door H2A.Z. Interessant genoeg werden geen andere histon-chaperones of chromatineremodelleringscomplexen gevonden. Nader onderzoek naar de rol van SWR1 in H2A.Z-regulatie wees uit dat SWR1 ervoor zorgt dat, tijdens S-fase (als er relatief veel nieuwe H2A.Z wordt aangemaakt) H2A wordt vervangen door H2A.Z, terwijl SWR1 er buiten S-fase (als er weinig H2A.Z wordt aangemaakt) voor zorgt dat eerder aanwezige H2A.Z behouden blijft.
Processen als DNA transcriptie, replicatie en reparatie komen allen tot stand uit een veelvoud van interacties tussen een groot aantal eiwitten. Wat deze processen reguleert op verschillende plekken in het genoom is grotendeels onbekend omdat tot nu toe de technieken ontbraken om dat op systematische wijze te bestuderen. Hoofdstuk 4 beschrijft Epi-Decoder, een op ChIP en barcoding gebaseerde sequencing technologie waarmee dergelijke vragen in gist beantwoord kunnen worden. In plaast van gebaseerd te zijn op massa-spectrometrie, zoals eerdere methodes, wordt gebruik gemaakt van DNA-sequencing. Vervolgens wordt Epi-Decoder toegepast op 3 verschillende loci in het genoom, waarmee een uitgebreid overzicht gegenereerd wordt van welke eiwit-interacties er op deze specifieke plekken plaatsvinden. Door gebruik te maken van veranderende fysiologische omstandigheden laten we zien dat we in staat zijn om dynamische chromatine-interacties te identificeren. Daarnaast hebben we laten zien dat met Epi-Decoder elk gewenste locus onderzocht kan worden. We laten daarvoor zien dat de benodigd barcode libraries kunnen worden gegenereerd door gebruik te maken van de CRISPR/Cas9-technologie.
In hoofdstuk 5 gebruiken we verbeterde Epi-Decoder-libraries om te laten zien hoe chromatine-eiwitinteracties op een actief getranscribeerd locus snel kunnen veranderen als RNA-polymerase II (PolII) geremd wordt door chemische of fysiologische signalen. We laten zien dat chemische remming van PolII leidt tot een snelle verandering in de lokale chromatine-eiwit-interacties. De binding van RNA-polymerase II nam snel af, waardoor factoren die een rol spelen bij transcriptie-elongatie en transcriptie-terminatie afnamen, terwijl metabole eiwitten en chromatineremodelleringscomplexen juist toenamen. Als transcriptie geremd wordt met fysiologische signalen, gaat dit gepaard met cel-specifieke repressie en verandering van metabole eiwitten en factoren die een rol spelen bij eiwitvouwing. Daarbij hebben we laten zien dat verschillende eiwitten uit hetzelfde complex of waarvan bekend is dat ze in hetzelfde proces een rol spelen, soms verschillende kinetiek vertonen. Dit duidt op een hierarchie tussen chromatinebindingsprocessen. Het blootleggen van dergelijke bindingsdynamiek van chromatine-eiwitten onder veranderende omstandigheden laat zien dat Epi-Decoder een krachtige strategie is om eiwit-eiwitinteracties en eiwitfuncties systematisch in kaart te brengen.
De hier ontwikkelde methodes Epi-ID en Epi-decoder zijn een aanvulling op het ‘Epi-discovery’ gereedschap, waarmee op een systematische manier chromatine-interacties in kaart gebracht kunnen worden.
Bekijk ook deze proefschriften
Structure-Preserving Data-Driven Methods for Modeling Turbulent Flows
Molecular insights into the role of VRS5 in tillering and lateral spikelet development in barley
Gamma Knife Radiosurgery for Skull Base Tumors
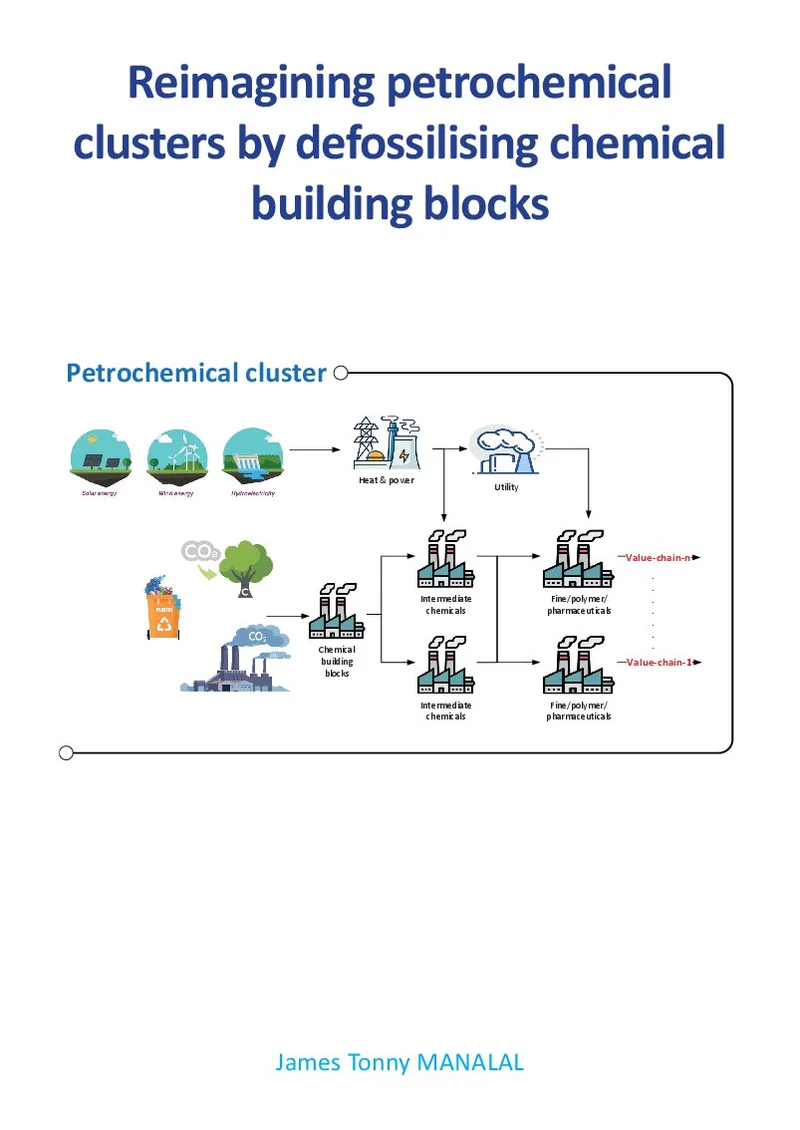
Reimagining petrochemical clusters by defossilising chemical building blocks
Microbial stabilization and protein functionality of plant-based liquids using pulsed electric fields
Wij drukken voor de volgende universiteiten